María Colomé: «Nuestra edad real depende de los interruptores que encienden o apagan nuestros genes»
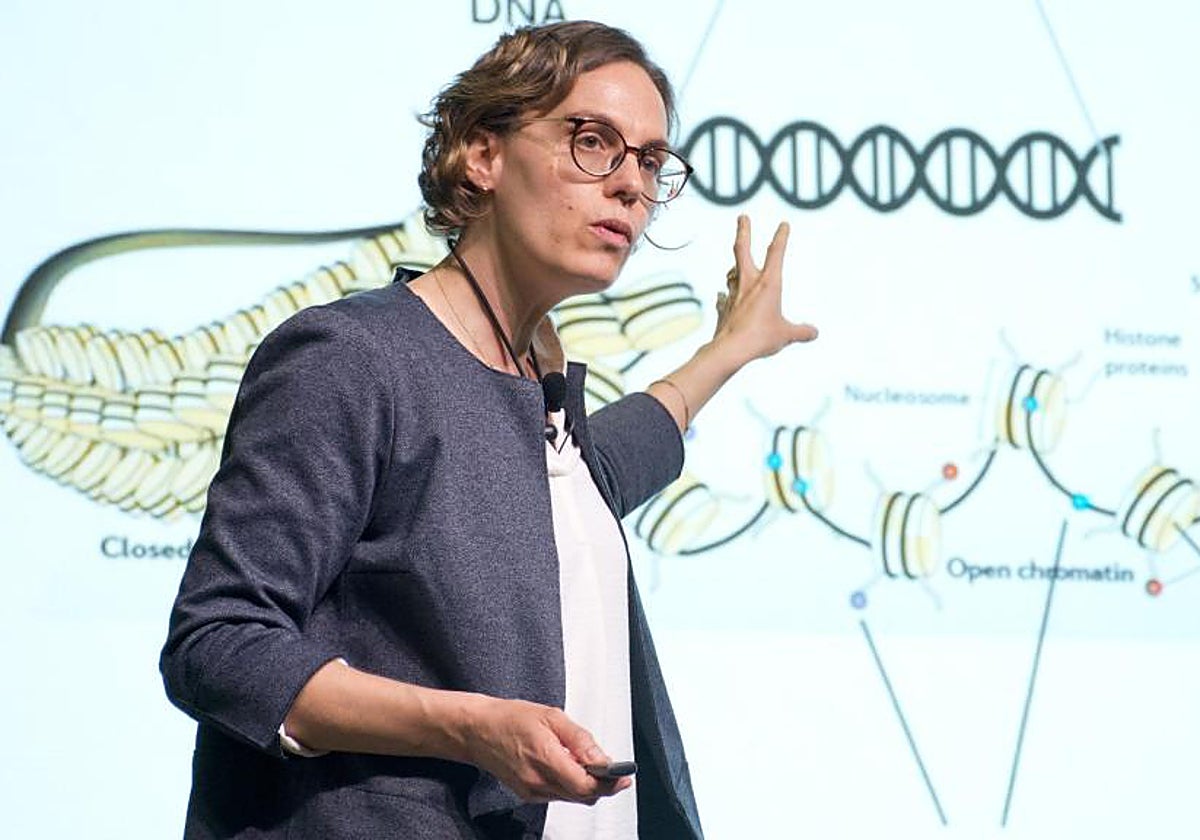
En el mundo de la biomedicina actual, el nivel de resolución es la nueva frontera. Durante décadas, la ciencia analizó los tejidos humanos como un bloque homogéneo, perdiendo los matices individuales de las unidades que nos componen. A caballo entre Alemania y España, la investigadora María Colomé Tatché se sitúa en la vanguardia de este cambio de paradigma . De visita en Madrid para participar en las jornadas «Ómicas de célula única y el Atlas Celular Humano: redefiniendo la biología de precisión», organizadas por la Fundación Ramón Areces , atiende a ABC para explicar cómo el análisis de célula única puede acabar revolucionando los tratamientos médicos. Física de formación pero dedicada a desentrañar los secretos de la vida a través de algoritmos, Colomé Tatché compagina su labor como profesora en la Ludwig Maximilian University de Múnich con su cargo de Investigadora Distinguida en el centro de investigación del Hospital del Mar de Barcelona. Su trabajo no se desarrolla entre probetas, sino entre millones de datos genómicos que la inteligencia artificial ayuda a procesar para responder, entre otras, a la pregunta del millón: ¿por qué una célula sana decide, de repente, ignorar las reglas y convertirse en tumoral? — Hasta hace poco, el análisis genómico se hacía en bloque, mezclando miles de células de un tejido. Ahora podemos mirar una a una. ¿Se podría comparar de pasar de ver la foto borrosa de una muchedumbre a entrevistar individualmente a cada individuo? — Un ejemplo que doy a menudo es la diferencia entre tomar un 'smoothie' o comerse una macedonia. Si una persona se toma un batido cada mañana y un día nota que no sabe bien, sabrá que algo está malo, pero no podrá identificar si es la fresa, el plátano o la manzana. En cambio, con una ensalada de frutas, puede decir: «Mira, era la fresa la que estaba en mal estado». Analizar a célula única permite exactamente eso. Hasta ahora podíamos decir que muchas enfermedades venían de un órgano —un cáncer o una dolencia degenerativa en el cerebro— pero no sabíamos exactamente qué célula era la que realmente estaba fallando. Ahora podemos comparar cada uno de los tipos celulares para ver cuál es el que está funcionando mal. — ¿Qué implica este nivel de detalle para el paciente, que aporta con respecto a analizar una molécula o un tejido? — Nos da la capacidad de avanzar en dos niveles. Primero, entender por qué aparecen las enfermedades y cómo prevenirlas a nivel molecular. Y segundo, llegar a tratamientos mucho menos invasivos y más personalizados. En lugar de una quimioterapia brutal que mate a todas las células, podremos dirigirnos únicamente a ese grupo de células particulares que sabemos que se están «portando mal». — Aquí entra en juego el concepto de heterogeneidad. Gracias a estas tecnologías reconocemos células que, al microscopio parecían iguales, pero se comportan de forma distinta. — Estamos desafiando lo que antes llamábamos «tipo celular». Cuando medimos un millón de células del cerebro, vemos que en lo que antes denominábamos simplemente «neurona» hay un montón de subtipos distintos. Incluso descubrimos células que parecen idénticas pero que, ante un tratamiento o una infección, responden de formas opuestas. Están «codificadas» para reaccionar de forma distinta aunque aparentemente hagan lo mismo que sus vecinas. — Para la medicina, ¿es una revolución similar a la que vivió la física hace un siglo con el descubrimiento del átomo? — Esta revolución está totalmente conducida por la tecnología. Gracias a que podemos medir células únicas vemos que los tejidos no son uniformes. De hecho, en las charlas científicas surge a menudo una discusión que podría durar horas: ¿Qué es realmente un tipo celular? Llega un punto en que no lo sabemos con certeza; es casi una cuestión de semántica. — Su trabajo se centra en la epigenómica, que es casi como tratar de entender esas reglas por las que una célula activa o no cada uno de sus interruptores. — Todas nuestras células tienen el mismo genoma, pero una célula del cerebro decide expresar genes distintos a una del corazón. ¿Cómo lo sabe? Gracias al epigenoma. Son modificaciones químicas y proteínas que se enganchan al genoma y le dicen: «Este gen aquí no se puede usar y este otro sí». Son, en efecto, como interruptores. Sin ellos, las células olvidarían cuál es su función. — Además de en la enfermedad, ¿influye todo esto en cómo envejecemos? — Sabemos que el envejecimiento es multifactorial, pero algo reconocido es que el epigenoma se va regulando cada vez peor cuando nos hacemos mayores. Existe la idea de rejuvenecer el epigenoma para que no seamos «tan mayores» biológicamente. No sabemos cómo tratarlo aún, pero hay marcas que nos dicen ya no nuestra edad cronológica, sino nuestra edad biológica. En cáncer, por ejemplo, ya existen fármacos que lo que hacen es cambiar o revertir ese epigenoma. — Su investigación tiene un pie en la biología y otro en la computación. ¿Cómo es el diálogo entre ambas disciplinas? — Estamos viviendo una gran revolución. Con los 'Foundation Models', unos LLM, como la arquitectura de los agentes de IA que usamos, entrenamos modelos con millones de datos genómicos sin necesidad de supervisión humana. Estas máquinas aprenden patrones que el cerebro humano es incapaz de detectar. Es, literalmente, un 'ChatGPT de la célula humana'. — ¿Podemos «preguntarle» cosas sobre la célula? — Sí, podemos preguntarle al modelo: «¿Qué pasaría si hubiera una mutación en este punto del genoma?». El reto ahora es la interpretabilidad. No queremos que la IA sea una «caja negra»; necesitamos entender por qué ha llegado a esa conclusión para comprender la causa real de una enfermedad. Por eso son tan importantes iniciativas como el Atlas del Genoma Humano, que obliga a que los datos sean públicos. Sin esa transparencia y generosidad entre científicos, los modelos no se pueden entrenar y la ciencia no avanzaría.